Aplicação de Modelos Mistos e SVM em Seleção Genômica de árvores de Eucalipto
DOI:
https://doi.org/10.29327/2520355.8.2-57Palavras-chave:
Seleção genômica, melhoramento genético, regressão ridge, validação cruzada, SVMResumo
Programas de melhoramento genético de árvores de floresta visam aumentar a
qualidade e ganho econômico de suas plantações por meio de manipulação genética.
Porém essa tarefa envolve desafios como longos ciclos de cruzamento e altos custos
de coleta de fenótipos. Nesse sentido, abordagens que avaliam valores genéticos de
árvores jovens sem a necessidade de fenotipagem, possuem o potencial de superar estes
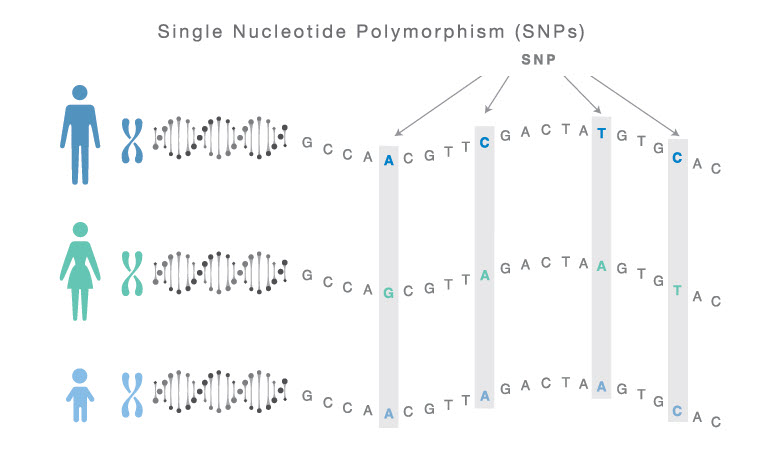
desafios. Uma delas é a Seleção Genômica, que consiste em se utilizar informações
moleculares para se estimar efeitos de marcadores genéticos com base em um modelo
de predição. O modelo, desenvolvido em uma população de treinamento com informações
genotípicas e fenotípicas, é utilizado para se obter valores genéticos baseados em dados
genotípicos de plantas candidatas. Portanto, a escolha do modelo é uma etapa essencial.
Este estudo compara modelos mistos e SVMs em dados de eucaliptos, além de avaliar fatores
que influenciam as métricas obtidas, como características genéticas, qualidade dos fenótipos
e efeitos de parentesco. Notou-se que os modelos para os fenótipos com maiores herdabilidades
apresentaram medidas de previsão superiores. Ainda foi possível verificar a importância do
controle dos efeitos de parentesco por meio da validação cruzada para a obtenção de métricas
menos otimistas, uma vez que os modelos são utilizados com dados de indivíduos não incluídos
na população de treinamento. Por fim, observou-se que os modelos de regressão e de SVM
apresentaram resultados consistentes, os quais evidenciaram que sua escolha deve depender
do estudo em questão.
Referências
BATES, Douglas; VAZQUEZ, Ana Ines. pedigreemm: Pedigree-based mixed-effects models. [S.l.], 2014. R package version 0.3-3.
CORTES, Corinna; VAPNIK, Vladimir. Support-vector networks. Machine learning, Springer, v. 20, n. 3, p. 273-297, 1995.
DESTA, Zeratsion Abera; ORTIZ, Rodomiro. Genomic selection: genome-wide prediction in plant improvement. Trends in Plant Science, v. 19, n. 9, p. 592-601, 2014. ISSN 1360-1385.
ENDELMAN, J. B. Ridge regression and other kernels for genomic selection with R package rrBLUP. Plant Genome, v. 4, p. 250-255, 2011.
GIANOLA, Daniel et al. Additive genetic variability and the Bayesian alphabet. Genetics, Genetics Soc America, v. 183, n. 1, p. 347-363, 2009.
GRATTAPAGLIA, D. Breeding forest trees by genomic selection: current progress and the way forward. In Genomics of Plant Genetic Resources Vol 1 pp 651-682. eds R. Tuberosa, A. Graner & E. Frison. [S.l.], 2014.
HENDERSON, Charles R. Selection index and expected genetic advance. Statistical genetics and plant breeding, Washington, DC, v. 982, p. 141-163, 1963.
JED WING, Max Kuhn. Contributions from et al. caret: Classification and Regression Training. [S.l.]. R package version 6.0-78.
LIMA, Bruno Marco de. Bridging genomics and quantitative genetics of Eucalyptus: genome-wide prediction and genetic parameter estimation for growth and wood properties using high-density SNP data. 2014. Tese (Doutorado) { Escola Superior de Agricultura "Luiz de Queiroz".
LIN, Z; HAYES, BJ; DAETWYLER, HD. Genomic selection in crops, trees and forages: a review. Crop and Pasture Science, CSIRO, v. 65, n. 11, p. 1177-1191, 2014.
MEYER, David; WIEN, FH Technikum. Support vector machines. R News, v. 1, n. 3, p. 23-26, 2001.
ORNELLA, L et al. Genomic-enabled prediction with classification algorithms. Heredity, Nature Publishing Group, v. 112, n. 6, p. 616, 2014.
R CORE TEAM. R: A Language and Environment for Statistical Computing. Vienna, Austria, 2017.
RESENDE, RT et al. Assessing the expected response to genomic selection of individuals and families in Eucalyptus breeding with an additive-dominant model. Heredity, Nature Publishing Group, v. 119, n. 4, p. 245, 2017.
ROBERTS, David R et al. Cross-validation strategies for data with temporal, spatial, hierarchical, or phylogenetic structure. Ecography, Wiley Online Library, v. 40, n. 8, p. 913-929, 2017.
SEARLE, Shayle R; CASELLA, George; MCCULLOCH, Charles E. Variance components. [S.l.]: John Wiley & Sons, 2009. v. 391.
SILVA-JUNIOR, OB et al. Eucalyptus genotyping taken to the next level: development of the "EucHIP60k. br"based on large scale multi-species SNP discovery and ascertainment, pp, 2013.
VANRADEN, Paul M. Efficient methods to compute genomic predictions. Journal of dairy science, Elsevier, v. 91, n. 11, p. 4414-4423, 2008.
WIMMER, Valentin et al. synbreed: a framework for the analysis of genomic prediction data using R. Bioinformatics, v. 28, n. 15, p. 2086-2087, 2012.
Downloads
Publicado
Como Citar
Edição
Seção
Licença
Proposta de Política para Periódicos de Acesso Livre
Autores que publicam nesta revista concordam com os seguintes termos:
- Autores mantém os direitos autorais e concedem à revista o direito de primeira publicação, com o trabalho simultaneamente licenciado sob a Licença Creative Commons Attribution que permite o compartilhamento do trabalho com reconhecimento da autoria e publicação inicial nesta revista.
- Autores têm autorização para assumir contratos adicionais separadamente, para distribuição não-exclusiva da versão do trabalho publicada nesta revista (ex.: publicar em repositório institucional ou como capítulo de livro), com reconhecimento de autoria e publicação inicial nesta revista.
- Autores têm permissão e são estimulados a publicar e distribuir seu trabalho online (ex.: em repositórios institucionais ou na sua página pessoal) a qualquer ponto antes ou durante o processo editorial, já que isso pode gerar alterações produtivas, bem como aumentar o impacto e a citação do trabalho publicado (Veja O Efeito do Acesso Livre).

